연구

< (왼쪽부터) 화학과 김우연 교수, 문석현 박사과정, 정원호 박사과정, 양수정 박사과정 >
우리 대학 연구진이 물리화학적 아이디어를 인공지능 딥러닝에 접목해 기존의 방법보다 일반화 성능이 높은 단백질-리간드 상호작용 예측 모델을 개발했다. 리간드란 수용체와 같은 큰 생체 분자에 특이적으로 결합하는 물질을 말하며, 생체 내의 중요한 요소이자 의약품의 개발 등에 큰 역할을 한다.
화학과 김우연 교수 연구팀이 교원창업 인공지능 신약 개발 스타트업 HITS 연구진과 함께 물리 기반 삼차원 그래프 심층 신경망을 이용해 일반화 성능을 높인 단백질-리간드 상호작용 예측 모델을 개발했다고 17일 밝혔다.
약물 후보 분자를 발굴하기 위해서 타깃 단백질과 강하게 결합하는 리간드를 찾는 것이 중요하다. 하지만 유효 물질을 찾기 위해 수백만에서 수천만 개의 무작위 리간드 라이브러리를 대상으로 실험 전수 조사를 수행하는 것은 천문학적인 시간과 비용이 필요하다. 이러한 시간과 비용을 절감하기 위해 최근 단백질-리간드 상호작용 예측에 기반한 가상탐색(virtual screening) 기술이 주목받고 있다.
기존의 상호작용 예측 인공지능 모델들은 학습에 사용한 구조에 대해서는 높은 예측 성능을 보여주지만, 새로운 단백질 구조에 대해서는 낮은 성능을 보이는 과적합(over-fitting)이 문제가 됐다. 과적합 문제는 일반적으로 모델의 복잡도에 비해 데이터가 적을 때 발생한다. 이번 연구는 이러한 과적합 문제를 해결함으로써 다양한 단백질에 대해 고른 성능을 보여주는 예측 모델을 개발하는데 주안점을 뒀다.
연구진은 물리화학적 아이디어들을 딥러닝 모델에 적용해 모델의 복잡도를 줄임과 동시에 물리 시뮬레이션을 통해 부족한 데이터를 보강함으로써 과적합 문제를 해결하고자 하였다. 단백질 원자와 리간드 원자 사이의 거리에 따른 반데르발스 힘, 수소 결합력 등을 물리화학적 방정식으로 모델링하고, 매개변수를 딥러닝으로 예측함으로써 물리 법칙을 만족하는 예측을 가능하게 했다.
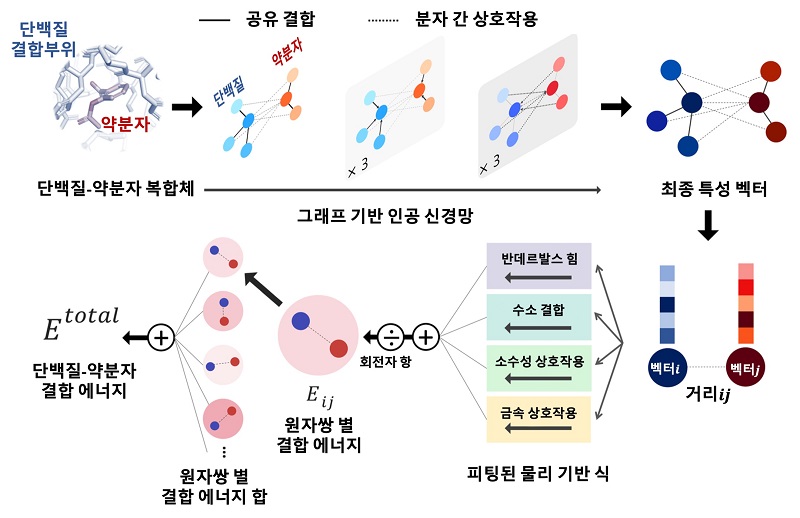
< 그림 1. 단백질-리간드 간 상호작용 예측 모델의 개요도 >
또한, 학습에 사용한 단백질-리간드 결정 구조가 실험적으로 판명된 가장 안정한 구조임에 착안했다. 부족한 실험 데이터를 보강하기 위해 불안정한 단백질-리간드 구조로 이루어진 수십만 개의 인공 데이터를 생성해 학습에 활용했고, 그 결과 생성된 구조에 비해 실제 구조를 안정하게 예측하도록 모델을 학습할 수 있었다.
연구진은 개발된 모델의 성능을 검증하기 위해 대조군으로 `CASF-2016 벤치마크'를 활용했다. 이 벤치마크는 다양한 단백질-리간드 구조들 사이에서 실험적으로 판명된 결정 구조에 근접한 구조를 찾는 도킹과 상대적으로 결합력이 큰 단백질-리간드 쌍을 찾는 스크리닝 등 실제 약물을 개발하는 과정에 필수적인 과제를 포함하고 있다. 검증 테스트 결과 기존에 보고된 기술에 비해 높은 도킹 및 스크리닝 성공률을 보여줬으며, 특히 스크리닝 성능은 기존에 보고된 최고 성능 대비 약 두 배 높은 수치를 보였다.
연구진이 개발한 물리 기반 딥러닝 방법론의 또 다른 장점은 예측의 결과를 물리적으로 해석 가능하다는 것이다. 이는 딥러닝으로 최적화된 물리화학 식을 통해 최종 상호작용 값을 예측하기 때문이다. 리간드 분자 내 원자별 상호작용 에너지의 기여도를 분석함으로써 어떤 작용기가 단백질-리간드 결합에 있어서 중요한 역할을 했는지 파악할 수 있으며, 이와 같은 정보는 추후 약물 설계를 통해 성능을 높이는 데 직접 활용할 수 있다.
공동 제1 저자로 참여한 화학과 문석현, 정원호, 양수정(현재 MIT 박사과정) 박사과정 학생들은 "데이터가 적은 화학 및 바이오 분야에서 일반화 문제는 항상 중요한 문제로 강조돼왔다ˮ며 "이번 연구에서 사용한 물리 기반 딥러닝 방법론은 단백질-리간드 간 상호작용 예측 뿐 아니라 다양한 물리 문제에 적용될 수 있을 것ˮ이라고 말했다.
한국연구재단의 지원을 받아 수행된 이번 연구는 국제 학술지 `Chemical Science(IF=9.825)' 2022년 4월 13호에 표지 논문 및 `금주의 논문(Pick of the Week)'으로 선정됐다. (논문명 : PIGNet: a physics-informed deep learning model toward generalized drug–target interaction predictions, 논문 링크 : https://doi.org/10.1039/D1SC06946B)
< 그림 2. 케미컬 사이언스 2022년 4월 13호의 표지 그림 >
-
연구 바이러스 면역반응‘켰다 껐다’단백질 스위치 발견
팬데믹 이후에도 다양한 신종 감염병이 출현하며 우리는 여전히 강력하고 지속적인 면역 방어를 요구하는 바이러스 위협에 직면해 있다. 동시에 과잉으로 면역 체계가 반응하면 오히려 몸의 조직을 해치는 부작용이 생기기도 한다. KAIST·국제 연구진이 이런 바이러스에 면역 반응을 조절하는 스위치 역할의 단백질을 찾아내는데 성공했다. 향후 감염병 대응과 자가면역질환 치료의 새로운 기반을 마련할 것으로 기대된다. 우리 대학 생명화학공학과 김유식 교수와 미국 플로리다주립대 차승희 교수 공동 연구팀이 세포 내 미토콘드리아에서 유래한 이중나선 RNA가 면역반응을 증폭시키는 메커니즘을 규명하고, 이를 조절하는 단백질 슬러프(SLIRP)가 바이러스 감염과 자가면역질환 양쪽에서 ‘면역 스위치’ 역할을 수행하는 것을 밝혀냈다. 자가면역질환은 면역 체계가 외부 침입자와 자기 조직을 구분하지 못하고 스스로를 공격하는 질환으로, 쉐그렌 증후군, 전신홍반루푸스 등으로 아
2025-05-14 -
연구 6밀리초에 단백질 반응 순간 포착 성공
생명현상을 이해하고 나아가 신약 개발을 위해 단백질 상호 작용 및 효소-기질 반응 등 마이크로초(micro-second)~밀리초(milli-second) 수준의 짧은 시간 동안 일어난 현상을 이해하는 것이 핵심이다. KAIST 연구진이 생명 현상을 이해하는데 필수적인 생화학 반응의 변화를 수 밀리초 수준에서 정지시키고 분석하는 방법을 개발했다. 우리 대학 화학과 강진영 교수와 물리학과 이원희 교수의 공동 연구팀이 초고속 생화학 반응 연구를 위한 ‘패릴렌(parylene)’* 기반 박막 미세유체 혼합-분사 장치’를 개발했다고 24일 밝혔다. *패릴렌: 단백질 반응을 초고속으로 관찰하기 위한 미세유체(microfluidics) 장치를 만드는 핵심 재료로 수 마이크로미터의 얇은 박막형태로 스프레이 제작이 가능하게 만든 소재임 이번 연구는 기존에 제시됐던 시간 분해 초저온 전자현미경(이하 TRCEM, Time-resolved cryo-elect
2025-03-24 -
연구 코로나바이러스 전염 메커니즘 규명
중증급성호흡기증후군(이하 SARS) 코로나바이러스와 같은 코로나 19(COVID-19)는 전 세계적 팬데믹으로 짧은 시간 안에 확산되었지만 왜 급격히 복제돼 빠르게 전염되는지 기전이 아직까지 규명되지 않았다. 우리 연구진이 코로나바이러스 핵심 효소 단백질(헬리케이스)의 복제과정이 급격히 촉진되어 전염되는 메커니즘을 밝혀내며 바이러스 백신 및 치료제 개발에 새로운 가능성을 제시했다. 우리 대학 생명과학과 이광록 교수 연구팀이 nsp13 단백질*은 두 가지 활성을 가지고 있어 시너지 효과를 내며, 이를 통해 SARS 코로나바이러스의 유전물질인 RNA 복제를 촉진한다는 기전을 규명했다고 17일 밝혔다. *nsp13 단백질: SARS 코로나바이러스의 헬리케이스로, 바이러스가 증식하는 데 필수적인 유전자 복제와 전사 과정에 중요한 효소이다. 헬리케이스는 마치 지퍼를 열고 닫는 것처럼 DNA나 RNA의 꼬인 구조를 풀어주는데, 유전정보를 읽거나 복제할 때 유전물질을 먼저 풀려야 하므로
2025-02-17 -
연구 선천성면역을 조절하는 인공단백질 디자인, 차세대 백신·면역 치료제 개발 가능성 제시
우리 대학 생명과학과 김호민 교수 연구팀과 국제 공동연구팀인 미국 워싱턴대학교 단백질디자인 연구소 (Institute for Protein Design, IPD) 닐 킹 교수 (Prof. Neil King) 연구팀은 컴퓨터기반 단백질디자인 기술을 활용하여 선천성면역을 활성화시키는 새로운 인공단백질을 디자인하고, 그들의 3차원 분자구조를 규명하는데 성공했다고 10일 밝혔다. 김호민 교수 연구팀과 Neil King 교수 연구팀은 컴퓨터 기반 단백질디자인 기술을 활용하여 선천성면역 수용체인 TLR3와 높은 친화도를 갖는 인공단백질을 개발했다. 또한, 초저온 투과전자현미경 (Cryo-EM) 분석을 통해 설계된 인공단백질이 TLR3와 결합하는 분자결합모드를 규명하였다. 특히, 자연계의 TLR3 작용제(dsRNA)와는 전혀 다른 구조를 가진 디자인된 인공단백질에 의해 선천성면역 수용체 TLR3을 효과적으로 활성화시킬 수 있음을 보인 첫 사례이다. 생명과학과 김호민 교수가 교신저자로 참
2025-02-10 -
연구 신개념 생체형틀법 캠바이오(CamBio) 개발
생물학적 구조는 인공적으로 복제하기 어려운 정도의 복잡한 특징을 가지고 있지만 이러한 생체 구조체를 직접적으로 활용여 제작하는 생체형틀법*은 다양한 분야의 응용으로 사용됐다. KAIST 연구진이 이전에 활용할 수 없었던 생체 구조체를 활용하고, 생체형틀법을 통해 적용될 수 있는 영역을 넓히는데 성공했다. *생체형틀법: 바이러스부터 우리의 몸을 구성하는 조직과 장기에 이르기까지 이러한 생체 구조의 기능을 활용하고자, 생체 구조를 형틀로 사용하여 기능성 구조재료를 만들어내는 방식 우리 대학 신소재공학과 장재범, 정연식 교수 공동연구팀이 생체 시료 안의 특정 내부 단백질을 활용하고 높은 조정성을 지닌 생체형틀법을 개발했다고 10일 밝혔다. 기존의 생체형틀법 방법은 주로 생체시료의 외부 표면만을 활용하거나, 한정된 치수와 샘플 크기로 인해 다양한 생체 구조체들의 구조-기능 상관성을 활용하여 기능성 나노구조체를 제작하기 어렵다는 한계를 가지고 있다. 이런 문제를 해결하고자 연
2025-01-10